Biplot do PCA incluir símbolo para os pontos
2 participantes
Página 1 de 1
 Biplot do PCA incluir símbolo para os pontos
Biplot do PCA incluir símbolo para os pontos
Boa tarde,
Minha base de dados está disposta da seguinte forma no arquivo 'variaveis.txt':
Amonia Nitrito Nitrato Ortofosfato SST TDS Salinidade Temperatura pH OD
E1 0.22 0.120 6,0 24.00 48.00 47.00 43.00 29.00 6.9 7.0
E2 0.23 1.193 8.0 23.00 51.00 49.00 47.00 29.20 6.8 6.4
E3 0.21 0.136 8.1 27.00 51.00 48.00 49.00 28.30 6.7 6.9
E4 0.53 0.648 7.0 26.00 51.00 52.00 50.00 27.30 6.5 6.8
C1 21.25 0.633 4.0 53.00 211.00 39.00 20.00 29.10 7.8 5.7
C2 26.27 0.190 8.6 63.00 351.00 32.00 24.00 29.70 6.5 4.2
C3 28.63 0.983 7.0 56.00 234.00 35.00 21.00 28.20 6.8 5.4
C4 35.29 1.145 6.2 64.00 341.00 24.00 22.00 26.10 7.7 5.3
Estou utilizando o script seguinte:
z<-read.table('variaveis.txt', header=T)
z
prc.z<-prcomp(z, scale=TRUE); prc.z
biplot pcr.z)
Preciso tornar os pontos E1, E2, E3, E4 representados por círculos todo preenchido com coloração verde. E C1, C2, C3 e C4 quadrados de outra cor também preenchidos com essa outra coloração.
Att. Roberta
Minha base de dados está disposta da seguinte forma no arquivo 'variaveis.txt':
Amonia Nitrito Nitrato Ortofosfato SST TDS Salinidade Temperatura pH OD
E1 0.22 0.120 6,0 24.00 48.00 47.00 43.00 29.00 6.9 7.0
E2 0.23 1.193 8.0 23.00 51.00 49.00 47.00 29.20 6.8 6.4
E3 0.21 0.136 8.1 27.00 51.00 48.00 49.00 28.30 6.7 6.9
E4 0.53 0.648 7.0 26.00 51.00 52.00 50.00 27.30 6.5 6.8
C1 21.25 0.633 4.0 53.00 211.00 39.00 20.00 29.10 7.8 5.7
C2 26.27 0.190 8.6 63.00 351.00 32.00 24.00 29.70 6.5 4.2
C3 28.63 0.983 7.0 56.00 234.00 35.00 21.00 28.20 6.8 5.4
C4 35.29 1.145 6.2 64.00 341.00 24.00 22.00 26.10 7.7 5.3
Estou utilizando o script seguinte:
z<-read.table('variaveis.txt', header=T)
z
prc.z<-prcomp(z, scale=TRUE); prc.z
biplot pcr.z)
Preciso tornar os pontos E1, E2, E3, E4 representados por círculos todo preenchido com coloração verde. E C1, C2, C3 e C4 quadrados de outra cor também preenchidos com essa outra coloração.
Att. Roberta
robertamfs- Mensagens : 32
Data de inscrição : 17/09/2018
 Re: Biplot do PCA incluir símbolo para os pontos
Re: Biplot do PCA incluir símbolo para os pontos
Oi, Roberta!
Nós vamos trabalhar com a PCA no módulo 6, quando estudarmos estatística multivariada, ok? Eu normalmente uso o pacote vegan para PCA e outras análises de ordenação. Então segue um exemplo usando este pacote, mostrando como alterar a coloração no biplot. O princípio é o mesmo que em qualquer gráfico, como nos gráficos de dispersão.
Basta copiar e colar o código, e usar como base, certo?
Nós vamos trabalhar com a PCA no módulo 6, quando estudarmos estatística multivariada, ok? Eu normalmente uso o pacote vegan para PCA e outras análises de ordenação. Então segue um exemplo usando este pacote, mostrando como alterar a coloração no biplot. O princípio é o mesmo que em qualquer gráfico, como nos gráficos de dispersão.
- Código:
library(vegan)
data(iris)
levels(iris$Species)
cores<-c("red4", "green4", "blue4")
resultado<-rda(iris[,1:4], scale=T)
biplot(resultado, display="species", xlim=c(-2, 3), ylim=c(-3, 1.5))
points(resultado, pch=16, col=cores[iris$Species])
legend("topright", pch=16, col=cores, legend=levels(iris$Species))
Basta copiar e colar o código, e usar como base, certo?
 Re: Biplot do PCA incluir símbolo para os pontos
Re: Biplot do PCA incluir símbolo para os pontos
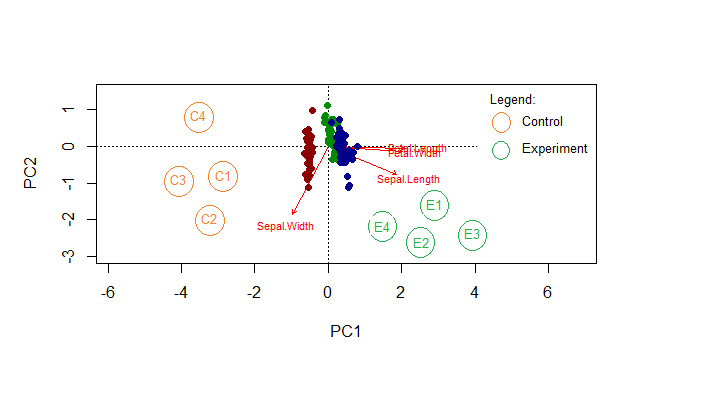
Grata professor. Deu certo, mas preciso de tipos de pontos que mostrem qual réplica é (C1,C2, C3 ou C4, E1, E2, E3 ou E4). Vou usar o exemplo da figura desse script do que preciso. E a legenda que não fique com linhas.
robertamfs- Mensagens : 32
Data de inscrição : 17/09/2018
robertamfs- Mensagens : 32
Data de inscrição : 17/09/2018
 Re: Biplot do PCA incluir símbolo para os pontos
Re: Biplot do PCA incluir símbolo para os pontos
Oi, Roberta, tudo bem?
Desculpe a demora. Continuo aqui resgatando as mensagens antigas sem resposta, certo?
Voltando a esta, a sua dúvida relacionada à "caixa" com a legenda. Como sempre, há vários caminhos distintos. Acabei de testar um que achei bem fácil, que é alterar as características da caixa dentro do comando legend. Fica assim (repetindo o exemplo anterior, mas adicionando apenas um argumento dentro de legend):
A adição foi do argumento box.lty=0, que determinou o tipo de linha usado na caixa que contorna a legenda.
Desculpe a demora. Continuo aqui resgatando as mensagens antigas sem resposta, certo?
Voltando a esta, a sua dúvida relacionada à "caixa" com a legenda. Como sempre, há vários caminhos distintos. Acabei de testar um que achei bem fácil, que é alterar as características da caixa dentro do comando legend. Fica assim (repetindo o exemplo anterior, mas adicionando apenas um argumento dentro de legend):
- Código:
library(vegan)
data(iris)
levels(iris$Species)
cores<-c("red4", "green4", "blue4")
resultado<-rda(iris[,1:4], scale=T)
biplot(resultado, display="species", xlim=c(-2, 3), ylim=c(-3, 1.5))
points(resultado, pch=16, col=cores[iris$Species])
legend("topright", pch=16, col=cores, legend=levels(iris$Species), box.lty=0)
A adição foi do argumento box.lty=0, que determinou o tipo de linha usado na caixa que contorna a legenda.
 Tópicos semelhantes
Tópicos semelhantes» Hiper Cubo latino, Método para seleção de pontos amostrais
» Plotagem de pontos em um mapa
» Modelagem de distribuição (Pontos de ocorrência)
» Qual a melhor maneira de resumir vários pontos em um único ponto na NMDS?
» Dica para fechamento da função par(mfrow...) - Util para RStudio com MARKDOWN
» Plotagem de pontos em um mapa
» Modelagem de distribuição (Pontos de ocorrência)
» Qual a melhor maneira de resumir vários pontos em um único ponto na NMDS?
» Dica para fechamento da função par(mfrow...) - Util para RStudio com MARKDOWN
Página 1 de 1
Permissões neste sub-fórum
Não podes responder a tópicos|
|
|